生体機能物質工学実験 II
0. プラスミドと EGFP の配列確認
はじめに
まず、この実習で使う GFP (EGFP)cDNA と、プラスミドの配列を確認しておきます。
配列についての正しい理解が以後の実験に欠かせません。配列情報の中で注目すべき
ところは制限酵素認識配列の位置や数、プロモーターや転写開始点、翻訳開始点、
終止コドン、さらに Kunkel 法による突然変異導入のために必要な配列などです。
知っておかなければならないこと
プラスミドはゲノム DNA と独立に複製する遺伝因子であるということを、「分子遺伝学 C」
で学びました。プラスミドは、遺伝子を単離したり切り貼りしたり細胞に導入するために
欠かせない道具となっています。そのため、配列にさまざまな手を加えられた、目的別の
プラスミドが多数市販されています。ここで用いるプラスミドは 2 種類です。一つは、
大腸菌を用いてタンパクを発現させるために開発された pQE30
(QIAGEN 社の製品)、
もう一つは、RNA プローブの合成や配列決定、一本鎖 DNA の調製等多目的に使用
される pBluescript II SK+
(Stratagene 社の製品)です。 pQE30 は、大腸菌を用いて
タンパクを発現させ、さらに発現させたタンパクを簡単に精製するための仕掛けが
施されています(この実習の後半で恩恵にあずかります)。タンパクの発現には適して
いますが、大腸菌細胞 1 個あたりのコピー数が非常に少ないため、プラスミドの精製や
配列決定などで苦労するかもしれません。 pBluescript II SK+ は、大腸菌細胞内での
コピー数が非常に多いので、大腸菌からのプラスミドの精製が容易です。
この実習では、pBluescript II SK+ に組み込んだ cDNA
を用いて部位
特異的突然変異法による変異導入を行った後、変異 cDNA を pQE30 に
組み込んで変異タンパクを発現させます。
今回使うプラスミドは、大腸菌の複製開始点(replication origin)とアンピシリン耐性
遺伝子(ampr)を持っています。これらのプラスミドを導入する大腸菌は、抗生物質
であるアンピシリンの存在下では増殖できず、死んで行きます。従って、大腸菌に
プラスミドを導入する操作をした後、アンピシリンを含む培養液で大腸菌を培養すれば
プラスミドがきちんと導入された大腸菌だけが生き残るという仕組みです。以後、プラスミド
をもつ大腸菌は常にアンピシリンを含む培地でプレッシャーをかけ続けなければいけ
ません。
この実習で使う GFP は正確に言うと野生型の GFP ではなくて、突然変異の入った
ものであり、EGFP と呼ばれています。 EGFP
についての詳しい説明は、別冊実験医学
ザ・プロトコルシリーズ 「non-RI 実験の最新プロトコール(蛍光の原理と実際:
遺伝子解析からバイオイメージングまで)」(編集/栗原靖之・武内恒成・松田洋一)
の第 4 章に載っていますので参考にしてください。
pQE30 の配列
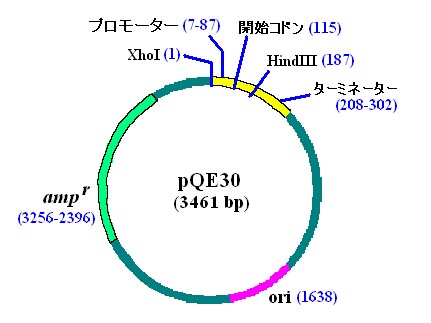
全長 3461 bp のプラスミドには大腸菌細胞内で複製起点(replication origin
= ori)
となる配列と、β-ラクタマーゼをコードするアンピシリン耐性遺伝子(ampr)があり
その他にタンパク発現用の仕掛けが組み込まれています。その部分の配列を下図に
示します。

制限酵素 XhoI による認識配列(CTCGAG)の直後から、バクテリオファージ T5
の
プロモーターの配列があります。プロモーターとオーバーラップして、lac
オペレーター
の配列が見られます。それぞれの配列の役割については「分子遺伝学 C」で学んだ
はずですので、復習しておいてください。転写開始点から
37 塩基下流に RBS という
配列(AAAGAGGAG)がありますね。RBS というのは ribosome-binding
site の
頭文字で、別名 Shine-Dalgarno 配列(SD 配列)です。そしてその直後に開始
コドンがあります。そのあとにヒスチジン(H)が連続した配列があります。これについて
は、この実習の後半で説明します。その後に、制限酵素 BamHI
の認識配列が
あります。そこから、制限酵素 HindIII
の認識配列までの間には、たくさんの制限酵素
認識配列があります。ここは、multi-cloning site
といって、この制限酵素を利用して
自分の興味のある cDNA などを組み込むのです。今回みなさんに使ってもらう
プラスミドでは、BamHI 配列と SmaI 配列の間に EGFP cDNA
が組み込んであります。
最後の HindIII 配列の直後から終止コドンが 3 つ並んでいます。自分の組み込んだ
cDNA が終止コドンを含んでいなくても、ここで必ず翻訳が終了するようにできています。
それに続いて転写終了のシグナルであるターミネーター配列がありますね。これらの
配列を確認しておいてください。
pBluescript II SK+ の配列
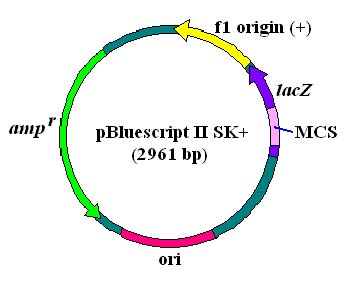
このプラスミドも pQE30 と同じ複製起点とアンピシリン耐性遺伝子を持っています。
従って、基本的なプラスミドの扱い方は pQE30 と同様と考えて間違いありません。
その他に気になるのは f1 origin (+)
と書いてある配列です。これが、部位特異的
突然変異の作製に重要な配列なのですが、詳しくは後で説明します。 MCS は
multi-cloning site (上にも出てきましたね)の略で、ここにはたくさんの制限酵素
認識配列があり、ここに cDNA や遺伝子断片を組み込むようになっています。
この部分は、実は lacZ 遺伝子の翻訳領域
N 末端付近にあたります。大腸菌の
正常な lacZ 遺伝子の翻訳領域は全長 3 kb ほどもあるのですが、このプラスミドに
組み込まれているのは正常な lacZ 遺伝子がコードする β-ガラクトシダーゼ
タンパクの一部分です。このプラスミドを導入する大腸菌の方は、本来もっている
lacZ 遺伝子に変異があり、pBluescript II SK+ によって持ち込まれる短いタンパクが
揃ってはじめて正常な酵素活性を示すようになるのです。プラスミドを導入した
大腸菌を培養する寒天培地に合成基質 5-bromo-4-chloro-3-indolyl-galactoside
(X-gal)を含ませておくと、できたコロニーが青くなります。これは、基質から
ガラクトシル基が除去された後の bromo-chloro-indole
が不溶性の青い沈殿に
なるためです。ところが、もしも MCS に cDNA が組み込まれると、lacZ 遺伝子の
コドンの読み枠(フレーム)がずれたり、途中に終止コドンができたりします。また、
たとえフレームがずれなかったとしても、長い挿入配列によって lacZ のコードする
ペプチドの立体構造が異常になるために酵素活性を持たないことになります。
そういうプラスミドが導入された大腸菌のコロニーは青くなりません。プラスミドに
外来 DNA を導入する実験では外来 DNA 導入がうまく行かず、元どおりの
pBluescript II SK+ が入った大腸菌ができてしまう場合があります。こういうとき、
プラスミドの導入操作をした後に X-gal を含む寒天培地に菌をまけば、
“白いコロニーを拾う” ことによって正しく組み立てられたプラスミドの選択を簡単に
行うことができます。 MCS 近傍の配列は以下のとおりです。
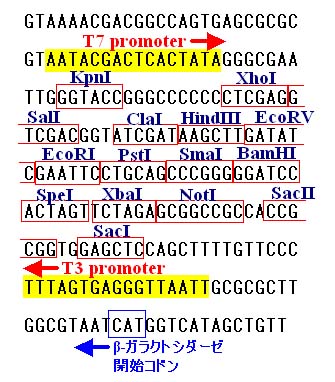
たくさんの制限酵素認識配列が並んでいるのがわかります。 HindIII
と BamHI の
認識配列に注意してください。これらの配列は、プラスミド上ではこの図に載っている
1 ケ所しかありません。
EGFP cDNA の配列
EGFP の翻訳領域の配列は以下のとおりです。
ATG GTG AGC AAG GGC GAG GAG CTG TTC ACC GGG GTG GTG
CCC ATC CTG GTC GAG CTG GAC 60
M V S K G E E L F T G V V P I
L V E L D 20
GGC GAC GTA AAC GGC CAC AAG TTC AGC GTG TCC GGC GAG GGC GAG GGC
GAT GCC ACC TAC 120
G D V N G H K F S V S G E G E
G D A T Y 40
GGC AAG CTG ACC CTG AAG TTC ATC TGC ACC ACC GGC AAG CTG CCC GTG
CCC TGG CCC ACC 180
G K L T L K F I C T T G K L P
V P W P T 60
CTC GTG ACC ACC CTG ACC TAC GGC GTG CAG TGC TTC AGC CGC TAC CCC
GAC CAC ATG AAG 240
L V T T L T Y G V Q C F S R Y
P D H M K 80
CAG CAC GAC TTC TTC AAG TCC GCC ATG CCC GAA GGC TAC GTC CAG GAG
CGC ACC ATC TTC 300
Q H D F F K S A M P E G Y V Q
E R T I F 100
TTC AAG GAC GAC GGC AAC TAC AAG ACC CGC GCC GAG GTG AAG TTC GAG
GGC GAC ACC CTG 360
F K D D G N Y K T R A E V K F
E G D T L 120
GTG AAC CGC ATC GAG CTG AAG GGC ATC GAC TTC AAG GAG GAC GGC AAC
ATC CTG GGG CAC 420
V N R I E L K G I D F K E D G
N I L G H 140
AAG CTG GAG TAC AAC TAC AAC AGC CAC AAC GTC TAT ATC ATG GCC GAC
AAG CAG AAG AAC 480
K L E Y N Y N S H N V Y I M A
D K Q K N 160
GGC ATC AAG GTG AAC TTC AAG ATC CGC CAC AAC ATC GAG GAC GGC AGC
GTG CAG CTC GCC 540
G I K V N F K I R H N I E D G
S V Q L A 180
GAC CAC TAC CAG CAG AAC ACC CCC ATC GGC GAC GGC CCC GTG CTG CTG
CCC GAC AAC CAC 600
D H Y Q Q N T P I G D G P V L
L P D N H 200
TAC CTG AGC ACC CAG TCC GCC CTG AGC AAA GAC CCC AAC GAG AAG CGC
GAT CAC ATG GTC 660
Y L S T Q S A L S K D P N E K
R D H M V 220
CTG CTG GAG TTC GTG ACC GCC GCC GGG ATC ACT CTC GGC ATG GAC GAG
CTG TAC AAG TAA 720
L L E F V T A A G I T L G M D
E L Y K * 239
開始コドンから終止コドンまでで 720 bp、239 アミノ酸のタンパクをコードしています。
L65 と T66 は、野生型 GFP ではそれぞれ F と S です。このミスセンス突然変異
によって、EGFP は野生型 GFP よりも明るい蛍光を発するようになっています。
この実習では、EGFP cDNA を pQE30 に組み込んだタンパク発現用プラスミドと
EGFP cDNA を pBluescript II SK+ に組み込んだ突然変異導入用プラスミドの
2 種類を使います。
EGFP と pQE30 との連結は(ある実験・・・今回の実習とは関係ありません・・・の目的上)
ちょっと複雑な形をしています。その配列は以下のとおりです。

pQE30 の BamHI 配列を利用して EGFP を組み込んでいますが、 BamHI 部位から
EGFP の第一メチオニンまでの間に短い挿入配列があります。この配列については
気にしないでください。一方、EGFP cDNA の後ろ側の配列は、終止コドンから少し
下流で、pQE30 の SmaI 配列に連結されていますが、この連結によって、もともとの
SmaI 部位(CCCGGG)の配列は変わってしまっており、再び SmaI で切断することは
できないようになっています。終止コドンの後ろから SmaI 連結部分までが 481 bp、
終止コドンの後ろから HindIII による切断部位までで 502 bp
あります。
従って、BamHI と HindIII によって切り出される
DNA 断片は 1275 bp です。
このことは後で必要になるのでよく憶えておいてください。
pQE30 に組み込まれた EGFP cDNA は、BamHI
と HindIII とで切断して、これを
pBluescript II SK+ に組み込みました。このとき、pBluescript II SK+ の方も、同様に
BamHI と HindIII とで切断しました。このことも重要ですから憶えておいてください。
上記のプラスミドおよび cDNA の配列はよーく頭に入れて実習に臨んでください。
制限酵素の性質や使い方については、この実習の後の方で学びます。
遺伝子工学的実験法の目次へ戻る





